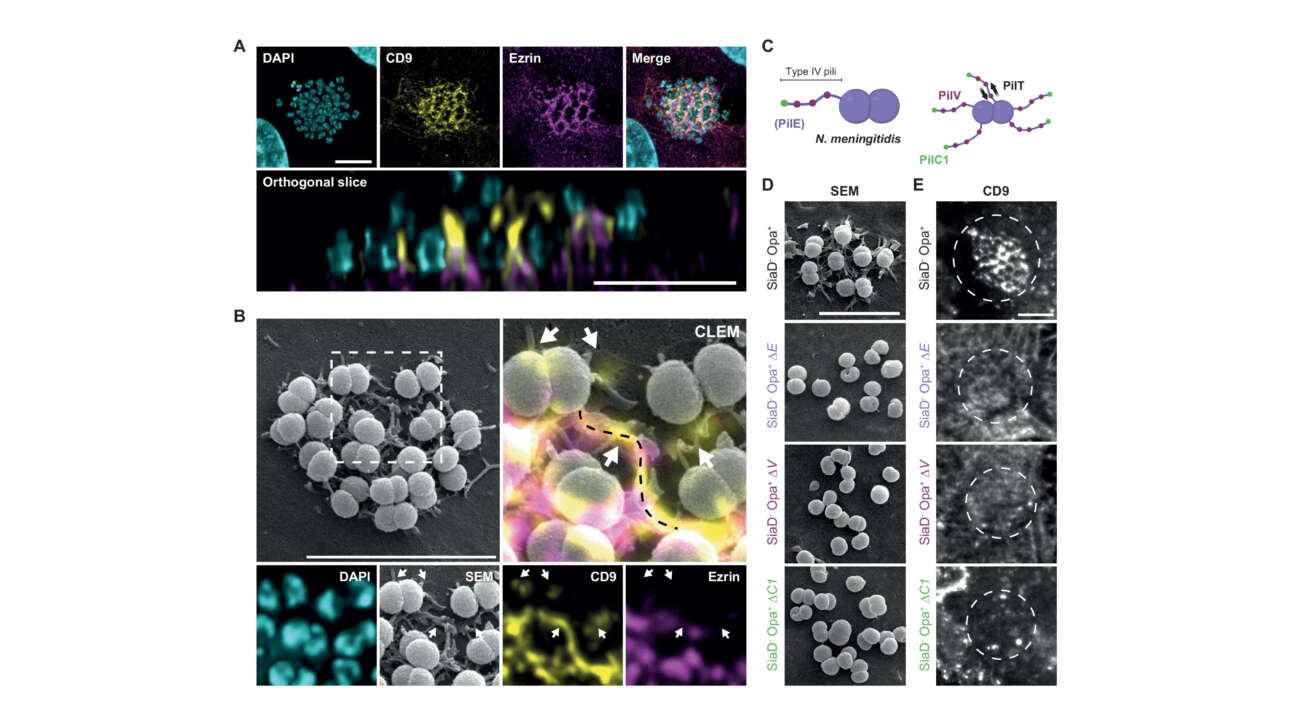
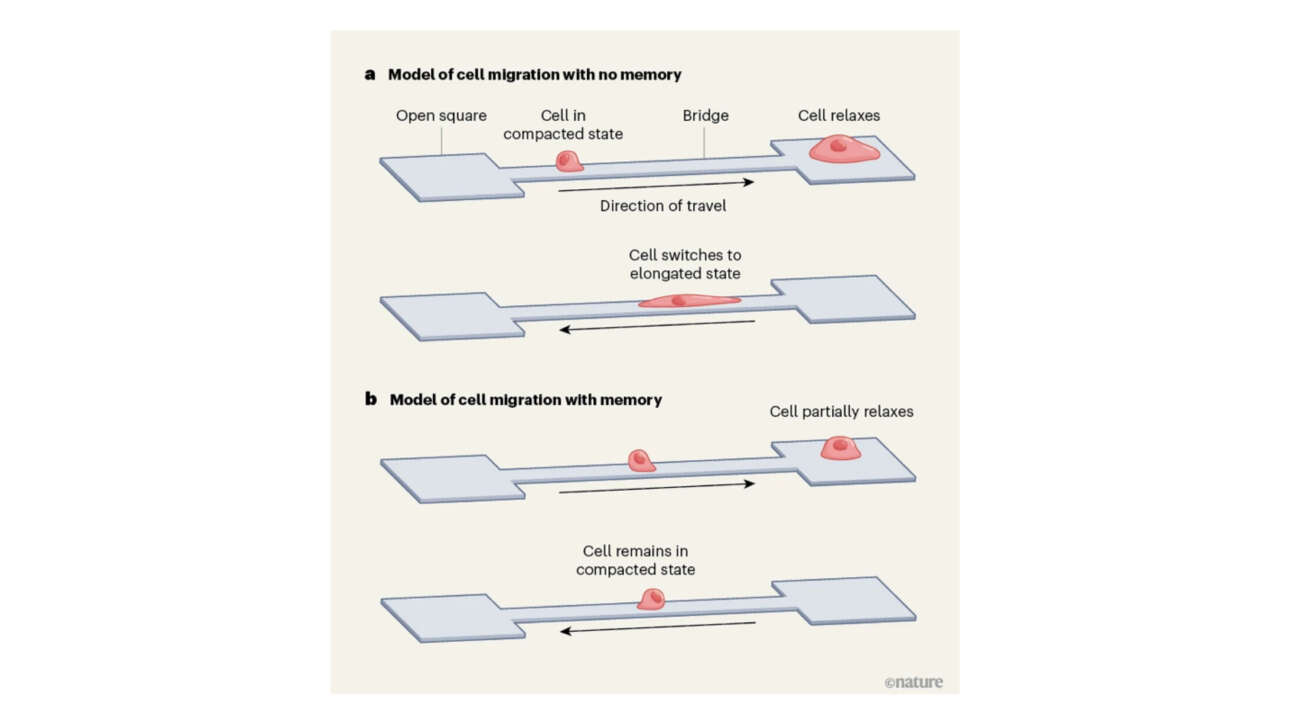
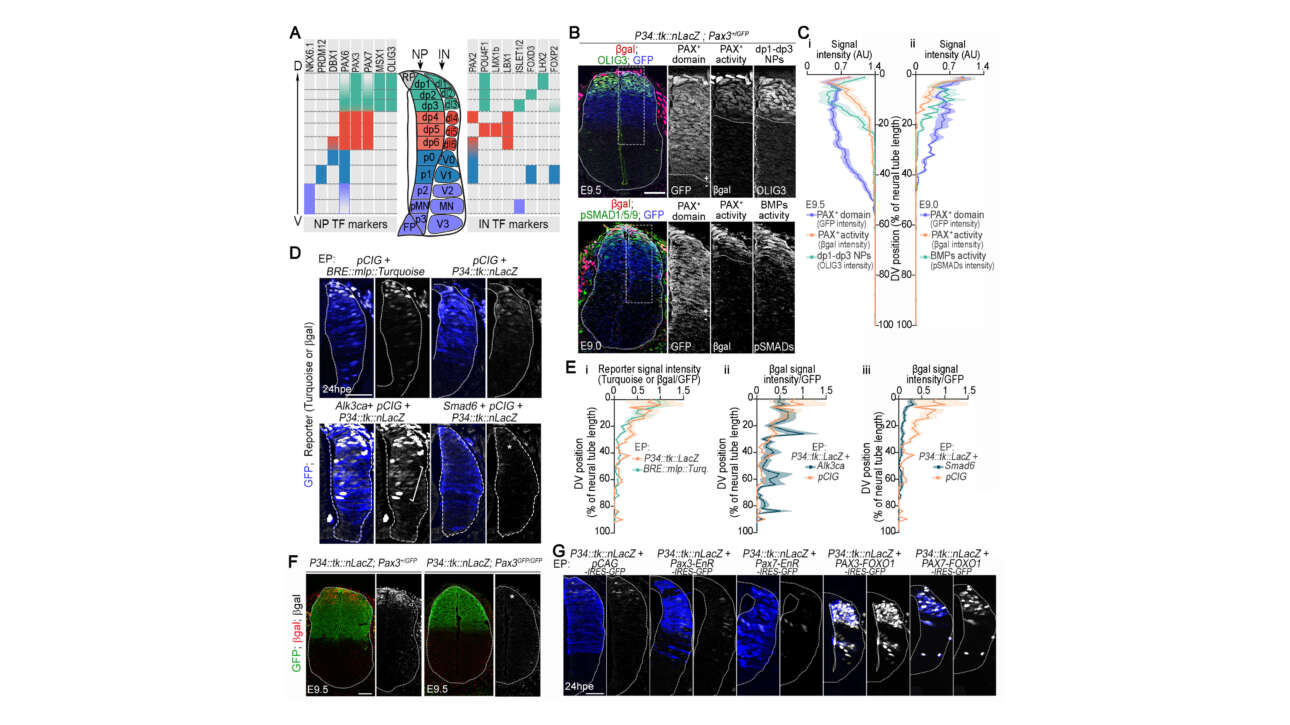
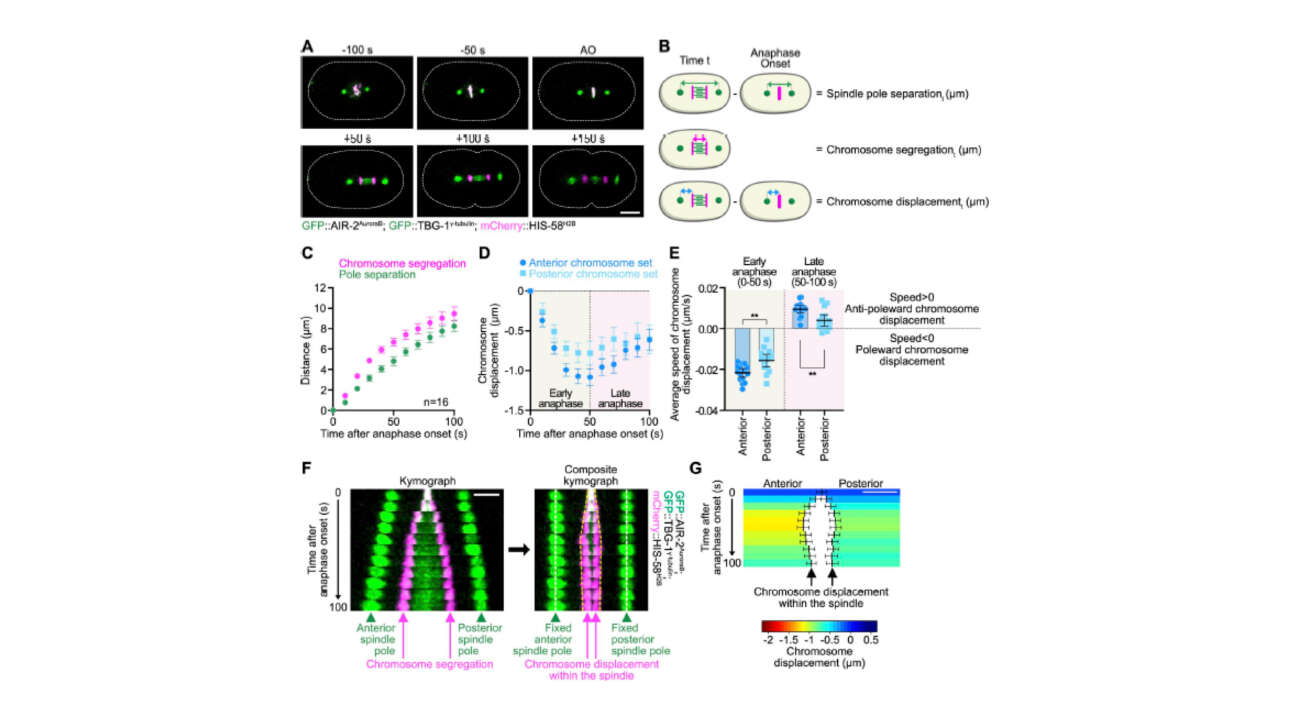
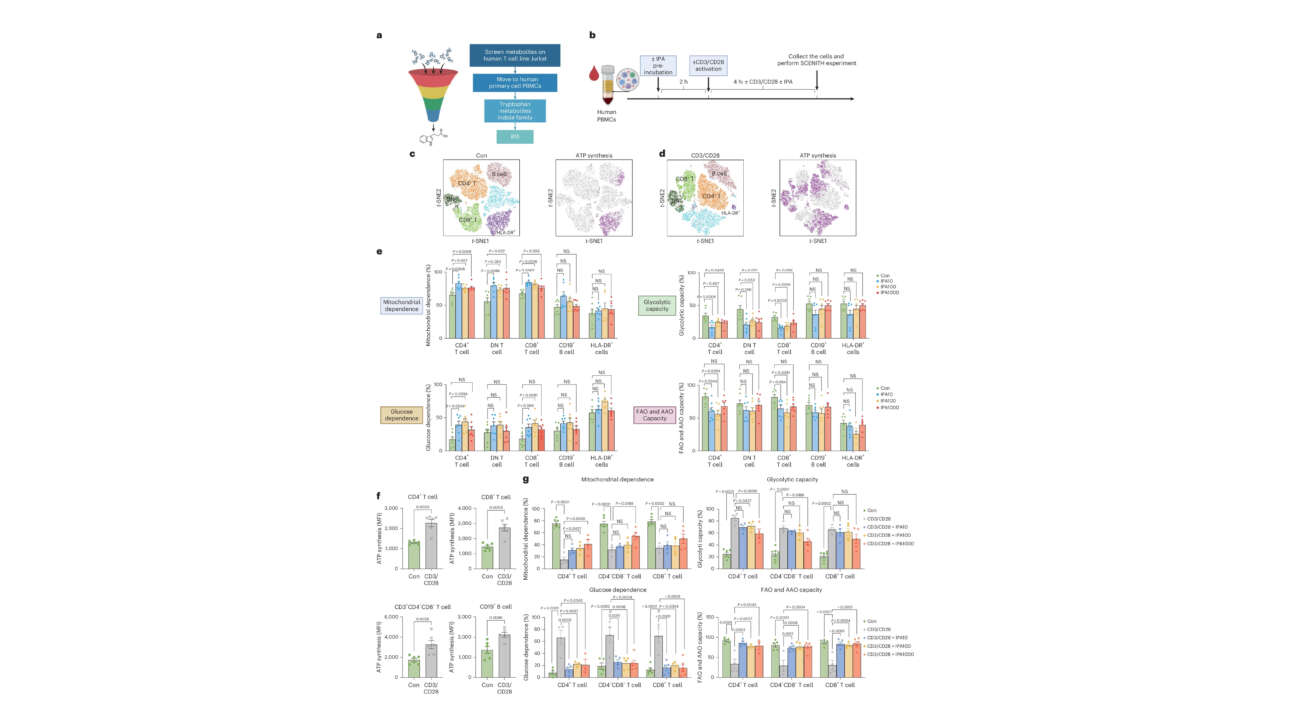
L'équipe Borghi a contribué à la publication d'un nouvel article dans Nature communications :
Meningococci drive host membrane tubulation to recruit their signaling receptors
Résumé :
Once passed into the bloodstream, bacterial pathogens have a limited time to interact with permissive receptors at the surface of host cells. Neisseria meningitidis has developed an extremely effective strategy allowing it to find its…