Paleogénomique
STEPHANE PEYREGNE

La compréhension de la biologie et de la santé humaines a progressé rapidement grâce à la richesse des données génomiques, médicales et fonctionnelles disponibles aujourd’hui. Une perspective évolutionniste enrichit ces travaux en éclairant les processus qui ont façonné notre biologie et en expliquant comment et pourquoi nous sommes devenus ce que nous sommes. En particulier, les génomes anciens, notamment ceux des Néandertaliens et des Dénisoviens, permettent d’accéder à des pans de notre évolution jusqu’alors inaccessibles avec les seules données actuelles. En intégrant ces génomes anciens aux données modernes, nous visons à identifier les modifications génétiques qui ont façonné la lignée humaine moderne et à étudier leur importance pour la biologie et la santé humaines.
Mots-clés : ADN ancien, évolution humaine, génomique évolutionnaire, paléogénomique, génétique des populations, Néandertaliens et Dénisoviens, sélection naturelle, introgression archaïque, maladies complexes, médecine évolutionnaire
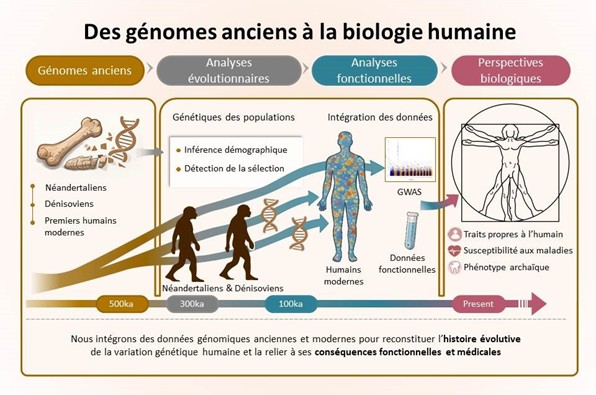
Nous étudions comment l’histoire évolutive de notre espèce a façonné la variation génétique humaine et ses conséquences pour la biologie et la santé. Les approches génomiques ont permis d’identifier de nombreux variants associés à des traits et des maladies, mais leur interprétation gagne à être replacée dans un cadre évolutionnaire explicite. En apportant cette perspective, nous cherchons à comprendre comment et pourquoi nos caractéristiques biologiques actuelles ont émergé.
Notre équipe s’appuie sur les génomes anciens pour accéder directement à des étapes passées de l’évolution humaine, inaccessibles avec les seules données actuelles. Ces données permettent de suivre, avec une résolution temporelle sans précédent, l’émergence, la persistance ou la disparition des variants génétiques. Nous nous intéressons notamment aux périodes anciennes de notre évolution, jusqu’à la divergence avec les humains archaïques, il y a plus de 500 000 ans, grâce à l’analyses des génomes néandertaliens et dénisoviens.
Nous générons et analysons ainsi des données paléogénomiques afin de reconstruire les trajectoires évolutives des variants génétiques. Nous développons des méthodes pour exploiter ces données, depuis leur authentification, notamment par l’estimation de la contamination, jusqu’à leur analyse évolutive, en reconstruisant l’histoire des populations et en détectant des signatures de sélection positive ancienne. Nous utilisons également des simulations pour tester la robustesse de ces méthodes et évaluer différents scénarios évolutifs. L’ensemble de ces analyses permet d’identifier les changements génétiques susceptibles d’avoir un impact fonctionnel important et de les distinguer de la majorité des variations neutres.
Nous relions ensuite ces trajectoires évolutives aux effets actuels des variants, en intégrant des données fonctionnelles et médicales. Cette approche permet notamment d’identifier les changements spécifiques à la lignée humaine moderne et d’éclairer leur contribution à l’émergence de traits propres à notre lignée. Elle offre également un cadre pour étudier l’origine évolutive des prédispositions aux maladies complexes — telles que les maladies auto-immunes, métaboliques ou psychiatriques — en distinguant les composantes anciennes du risque, issues de compromis évolutifs, des contributions plus récentes liées à l’accumulation de variants faiblement délétères dans des contextes de sélection naturelle sous-optimale au cours de notre histoire démographique.
Par ailleurs, nous développons des approches visant à inférer des caractéristiques phénotypiques passées, en particulier chez les humains archaïques, à partir des génomes anciens et des effets de l’ascendance archaïque observés dans les populations actuelles. Ces méthodes permettent d’accéder à des traits absents du registre fossile et de mieux situer les spécificités de notre lignée. En collaboration avec des paléoanthropologues et des généticiens, nous validons ces approches sur des traits bien documentés, tels que la morphologie dentaire, et les appliquons notamment à l’étude de l’évolution du système immunitaire.
En reliant données paléogénomiques, modèles évolutifs et informations fonctionnelles et médicales, notre objectif est d’identifier les mécanismes ayant façonné la variation génétique humaine et de mieux comprendre comment notre histoire évolutive continue d’influencer notre biologie et notre santé.
Pour contacter un membre de l’équipe par mail : prenom.nom@ijm.fr
Yang, J., Iasi, L.N.M., Fu, Q., Cooke, N.P., Kelso, J., Peyrégne, S.*, Peter, B.M.* (2025), An early East Asian lineage with unexpectedly low Denisovan ancestry, Current Biology (* – equally contributing authors).
Swiel, Y., Kelso, J., Peyrégne, S. (2025), Resolving the source of branch length variation in the Y chromosome phylogeny, Genome Biology.
Peyrégne, S., Slon, V., Kelso, J. (2024), More than a decade of genetic research on the Denisovans, Nature Reviews Genetics
Peyrégne, S., Kelso, J., Peter, B.M., Pääbo, S. (2022), The evolutionary history of human spindle genes includes back-and-forth gene flow with Neandertals, eLife.
Peyrégne, S., Slon, V., Mafessoni, F., de Filippo, C., Hajdinjak, M., Nagel, S., Nickel, B., Essel, E., Le Cabec, A., Wehrberger, K., Conard, N.J., Kind, C. J., Posth, C., Krause, J., Abrams, G., Bonjean, D., Di Modica, K., Toussaint, M. Kelso, J., Meyer, M., Pääbo, S., Prüfer, K. (2019), Nuclear DNA from two early Neandertals reveals 80,000 years of genetic continuity in Europe, Science Advances, 5 (6), eaaw5873
Peyrégne, S., Boyle, M., Dannemann, M., Prüfer, K. Detecting ancient positive selection in humans using extended lineage sorting. (2017), Genome Research 27 (9), 1563-157
Massilani, D., Peyrégne, S., Iasi, L. N. M., de Filippo, C., Mafessoni, F., Bossoms Mesa, A., Sümer, A. P., Swiel, Y., Popli, D., Silverman, S., Boyle, M. J., Kozlikin, M. B., Shunkov, M. V., Derevianko, A. P., Higham, T., Douka, K., Meyer, M., Zeberg, H., Kelso, J., & Pääbo, S. (2026). A high-coverage Neandertal genome from the Altai Mountains reveals population structure among Neandertals. Proceedings of the National Academy of Sciences, 123(13), e2534576123. https://doi.org/10.1073/pnas.2534576123
Yang, J., Iasi, L.N.M., Fu, Q., Cooke, N.P., Kelso, J., Peyrégne, S.*, Peter, B.M.* (2025), An early East Asian lineage with unexpectedly low Denisovan ancestry, Current Biology (* – equally contributing authors).
Jacobs, Z., Zavala, E.I., Li, B., O’Gorman, K., Shunkov, M.V., Kozlikin, M.B., Derevianko, A.P., Uliyanov, V., Goldberg, P., Agadjanian, A., Vasiliev, S., Brink, F., Peyrégne, S., Slon, V., Pääbo, S., Kelso, J., Meyer, M., Roberts, R. (2025), Pleistocene chronology and history of hominins and fauna at Denisova Cave, Nature Communications.
Swiel, Y., Kelso, J., Peyrégne, S. (2025), Resolving the source of branch length variation in the Y chromosome phylogeny, Genome Biology.
Sümer, A.P., Rougier, H., Villalba-Mouco, V., Huang, Y., Iasi, L.N.M., Essel, E., Bossoms Mesa, A., Furtwaengler, A., Peyrégne, S., de Filippo, C., Rohrlach, A.B., Pierini, F., Mafessoni, F., Fewlass, H., Elena I. Zavala, E.I., Mylopotamitaki, D., Bianco, R.A., Schmidt, A., Zorn, J., Nickel, B., Patova, A., Posth, C., Smith, G.M., Ruebens, K., Sinet-Mathiot, V., Stoessel, A., Dietl, H., Jörg Orschiedt, J., Kelso, J., Zeberg, H., Bos, K.I., Welker, F., Weiss, M., McPherron, S., Schüler, T., Hublin, J.J., Velemínský, P., Brůžek, J., Peter, B.M., Meyer, M., Meller, H., Ringbauer, H., Hajdinjak, M., Prüfer, K., Krause, J. (2024), Earliest modern human genomes constrain timing of Neandertal admixture, Nature.
Peyrégne, S., Slon, V., Kelso, J. (2024), More than a decade of genetic research on the Denisovans, Nature Reviews Genetics
Popli, D., Peyrégne, S., Peter, B.M. (2023), KIN: A method to infer relatedness from low-coverage ancient DNA, Genome Biology.
Peyrégne, S., Kelso, J., Peter, B.M., Pääbo, S. (2022), The evolutionary history of human spindle genes includes back-and-forth gene flow with Neandertals, eLife.
Skov, L., Peyrégne, S., Popli, D., Iasi, L.N.M., Devièse, T., Slon, V., Zavala, E.I., Hajdinjak, M., Sümer, A., Grote, S., Bossoms Mesa, A., López Herráez, D., Nickel, B., Nagel, S., Richter, J., Essel, E., Gansauge, M., Schmidt, A., Korlević, P., Comeskey, D., Derevianko, A.P., Kharevich, A., Markin, S.V., Talamo, S., Douka, K., Krajcarz, M.T., Roberts, R.G., Higham, T., Viola, B., Krivoshapkin, A.I., Kolobova, K.A., Kelso, J., Meyer, M., Pääbo, S., Peter B.M. (2022), Genetic insights into the social organization of Neanderthals, Nature.
Peyrégne, S., Peter, B.M. (2020), AuthentiCT: a model of ancient DNA damage to estimate the proportion of present-day DNA contamination, Genome Biology.
Khan, N., de Manuel, M., Peyrégne, S., Do, R., Prüfer, K., Marques-Bonet, T., Varki, N., Gagneux, P., & Varki, A. (2020). Multiple Genomic Events Altering Hominin SIGLEC Biology and Innate Immunity Predated the Common Ancestor of Humans and Archaic Hominins. Genome biology and evolution.
Romandini, M., Oxilia, G., Bortolini, E., Peyrégne, S., Delpiano, D., Nava, A., Panetta, D., Di Domenico, G., Martini, P., Arrighi, S., Badino, F., Figus, C., Lugli, F., Marciani, G., Silvestrini, S., Menghi Sartorio, J.C., Terlato, G., Hublin, J.J., Meyer, M., Bondioli, L., Higham, T., Slon, V., Peresani, M., Benazzi, S. (2020), A late Neanderthal tooth from northeastern Italy, Journal of Human Evolution 147, 102867
Peyrégne, S., Prüfer, K. (2020), Present‐Day DNA Contamination in Ancient DNA Datasets, BioEssays, 2000081
Mafessoni, F., Grote, S., de Filippo, C., Slon, V., Kolobova, K. A., Viola, B., Markin, S. V., Chintalapati, M., Peyrégne, S., Skov, L., Skoglund, P., Krivoshapkin, A. I., Derevianko, A. P., Meyer, M., Kelso, J., Peter, B., Prüfer, K., & Pääbo, S. (2020). A high-coverage Neandertal genome from Chagyrskaya Cave. Proceedings of the National Academy of Sciences, 117(26), 15132–15136. https://doi.org/10.1073/pnas.2004944117
Bokelmann, L., Hajdinjak, M., Peyrégne, S., Brace, S., Essel, E., de Filippo, C., Glocke, I., Grote, S., Mafessoni, F., Nagel, S., Kelso, J., Prüfer, K., Vernot, B., Barnes, I., Pääbo, S., Meyer, M., Stringer, C. (2019), A genetic analysis of the Gibraltar Neanderthals, Proceedings of the National Academy of Sciences 116 (31), 15610-15615
Peyrégne, S., Slon, V., Mafessoni, F., de Filippo, C., Hajdinjak, M., Nagel, S., Nickel, B., Essel, E., Le Cabec, A., Wehrberger, K., Conard, N.J., Kind, C. J., Posth, C., Krause, J., Abrams, G., Bonjean, D., Di Modica, K., Toussaint, M. Kelso, J., Meyer, M., Pääbo, S., Prüfer, K. (2019), Nuclear DNA from two early Neandertals reveals 80,000 years of genetic continuity in Europe, Science Advances, 5 (6), eaaw5873
Laval, G., Peyrégne, S., Zidane, N., Harmant, C., Renaud, F., Patin, E., Prugnolle, F., Quintana-Murci, L. (2019), Recent Adaptive Acquisition by African Rainforest Hunter-Gatherers of the Late Pleistocene Sickle-Cell Mutation Suggests Past Differences in Malaria Exposure, The American Journal of Human Genetics 104 (3), 553-561
Slon, V. *, Mafesonni, F.*, Vernot, B. *, de Filippo, C., Grote, S., Viola, B., Hajdinjak, M., Peyrégne, S., Nagel, S., Brown, S., Douka, K., Higham, T., Kozlikin, M.B., Shunkov, M.V., Derevianko, A.P., Kelso, J., Meyer, M., Prüfer K. and Pääbo S. (2018), The genome of the offspring of a Neanderthal mother and a Denisovan father, Nature 561 (7721), 113 (* – equally contributing authors)
Prüfer, K., de Filippo, C. *, Grote, S. *, Mafessoni, F. *, Korlević, P., Hajdinjak, M., Vernot, B., Skov, L., Hsieh, P., Peyrégne, S., Reher, D., Hopfe, C., Nagel, S., Maricic, T., Fu, Q., Theunert, C., Rogers, R., Skoglund, P., Chintalapati, M., Dannemann, M., Nelson, B.J., Key, F.M., Rudan, P., Kućan, Ž., Gušić, I., Golovanova, L.V., Doronichev, V.B., Patterson, N., Reich, D., Eichler, E.E., Slatkin, M., Schierup, M.H., Andrés, A.M., Kelso, J., Meyer, M., Pääbo, S. (2017), A high-coverage Neandertal genome from Vindija Cave in Croatia, Science 358 (6363), 655-658 (* – equally contributing authors)
Peyrégne, S., Boyle, M., Dannemann, M., Prüfer, K. Detecting ancient positive selection in humans using extended lineage sorting. (2017), Genome Research 27 (9), 1563-157
- Diego López-Onaindia (Catalan Institute of Human Paleoecology and Social Evolution)
- Kim Genuite (Université de Bordeaux)
- Lluis Quintana-Murci (Institut Pasteur)
- Marie-Hélène Moncel (Muséum National d’Histoire Naturelle)
- Stéphanie Le Hellard (University of Bergen)
2026-2029 : Fondation pour la Recherche Médicale
2026-2028 : Financement “Crossing Cutting Edges” (Université Paris Cité)
9/01/2026 : Stéphane Peyrégne, responsable d’équipe au sein de l’institut, est lauréat du prix Georges Brahms 2025 décerné par la fondation CNRS



